ApiEve – Identification d’une souche
Contexte
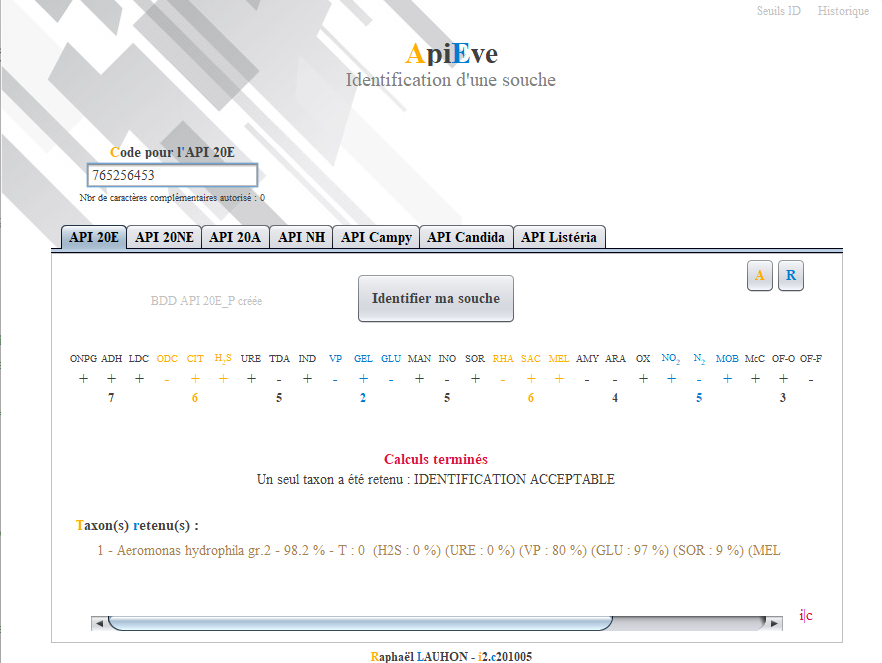
ApiEve est une application conçue pour faciliter l’identification d’une souche à partir des galeries API (Analytical Profil Index) utilisées en microbiologie. Elle s’appuie sur un principe simple : l’utilisateur saisit le code numérique obtenu après lecture des tests biochimiques, l’application le transforme en une chaîne « + / - », puis interroge des bases de données de référence afin de calculer des taux de correspondance et de proposer les taxons les plus probables.
L’outil est structuré autour de trois composants qui communiquent entre eux : une interface graphique, un programme qui exécute les contrôles, requêtes et calculs, et des bases de données qui stockent les valeurs nécessaires à l’identification.
ApiEve a également été pensée pour un usage en contexte contraint : les bases de données peuvent être déployées localement lorsque l’accès Internet n’est pas disponible, tout en conservant le même fonctionnement.
Accéder à la vidéo de démonstration en cliquant ici
Illustration
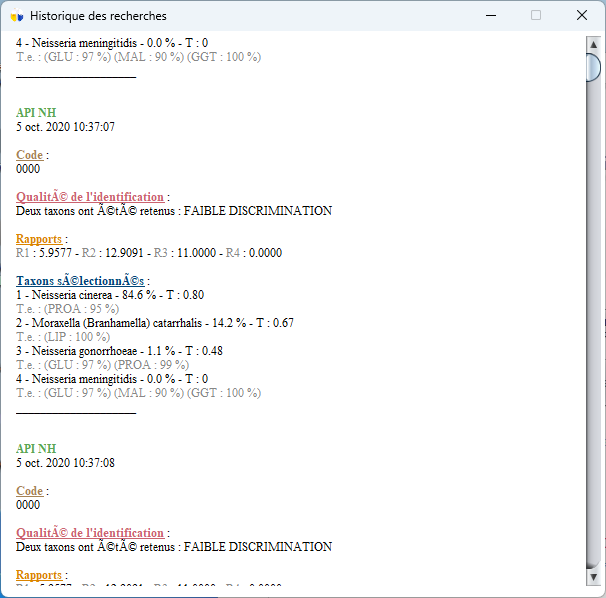
Historique des recherches sauvegardées
Missions réalisées
- Conception de la logique d’identification : saisie du code → profil « + / - » → calculs → résultats
- Développement en Java de l’interface et des contrôles de saisie (formats, cas particuliers, messages d’état)
- Connexion aux bases de données et gestion d’une base de travail temporaire pour les calculs
- Implémentation des calculs : correspondances test par test, indice T, seuils de qualité et cas de discrimination
- Ajout d’outils d’usage : historique, affichage des seuils/BDD, diagnostic et réinitialisation
Compétences mobilisées
- Conception fonctionnelle d’un outil métier
- Développement d’une application en Java
- Structuration d’algorithmes de décision
- Gestion de bases de données et requêtes
- Ergonomie d’interface (retours utilisateurs, messages d’état)
- Formalisation de documentation d’utilisation
Apports du projet
ApiEve apporte un gain d’efficacité pour l’identification en automatisant la comparaison aux données de référence et en rendant visibles les étapes clés (chaîne « + / - », progression des calculs, qualité d’identification).
Le projet met aussi en évidence une démarche d’amélioration continue : l’application explicite les limites possibles et propose des outils de diagnostic (tests à l’encontre, historique, états de connexion).
Ce projet m’a apporté une méthododologie de travail : partir d’un besoin terrain, traduire un raisonnement microbiologique en logique algorithmique fiable, puis le rendre compréhensible pour l’utilisateur. Il a renforcé ma capacité à concevoir un outil métier robuste (contrôles, traçabilité, maintenabilité) et directement utilisable en contexte professionnel.